คำอธิบาย
ไฮฟ์ เอ็นจีเอสทีเอ็ม OnePot Pro DNA Library Prep Kit V3 เป็นชุดเตรียมไลบรารีที่ใช้การแยกส่วนเอนไซม์รุ่นใหม่ พัฒนาและออกแบบโดยเฉพาะสำหรับ อิลลูมิน่า แพลตฟอร์มการจัดลำดับ &MGI เมื่อเปรียบเทียบกับวิธีการสร้างห้องสมุดแบบดั้งเดิม ผลิตภัณฑ์นี้ใช้เอนไซม์การแยกส่วนที่มีคุณภาพสูง ซึ่งช่วยขจัดขั้นตอนอัลตราโซนิกที่ยุ่งยาก นอกจากนี้ยังช่วยลดความยุ่งยากในการทำงานโดยรวมโมดูลการแยกส่วนและการซ่อมแซมปลายเข้าเป็นหนึ่งเดียว นอกจากนี้ เอนไซม์และบัฟเฟอร์สำหรับโมดูลการผูกมัดยังได้รับการผสมไว้ล่วงหน้า ซึ่งช่วยลดเวลาและต้นทุนในการสร้างห้องสมุดได้อย่างมาก ทำให้เหมาะสำหรับการสร้างห้องสมุดอัตโนมัติมากขึ้น ชุดเตรียมห้องสมุดนี้มีอัตราการแปลงห้องสมุดที่ยอดเยี่ยมและใช้ได้กับตัวอย่างจากสัตว์ พืช จุลินทรีย์ทั่วไป ฯลฯ และยังรวมถึงตัวอย่าง FFPE อีกด้วย ผลิตภัณฑ์นี้แสดงให้เห็นถึงประสิทธิภาพที่สูงขึ้นในการแบ่งส่วนโดยอิงจากชุดการสร้างห้องสมุดรุ่นก่อนหน้า การซ่อมแซมปลายสาย การแยกส่วน dA และการผูกอะแดปเตอร์มากกว่ารุ่นก่อนหน้า เอนไซม์ที่มีความเที่ยงตรงสูงช่วยปรับปรุงความสม่ำเสมอและความเที่ยงตรงของการขยายสัญญาณได้อย่างมีนัยสำคัญ
ข้อมูลจำเพาะ
| เลขที่แมว | 12194ES08 / 12194ES24 - 12194ES96 |
| ขนาด | 8 ที/24 ต / 96 ที |
ส่วนประกอบ
| ส่วนประกอบ หมายเลข | ชื่อ | 12194ES08 | 12194อีเอส24 | 12194ES96 |
| 12194-ก | สเมียร์เรสทีเอ็ม บัฟเฟอร์ 3.0 | 80 ไมโครลิตร | 240 ไมโครลิตร | 960 ไมโครลิตร |
| 12194-ข | สเมียร์เรสทีเอ็ม เอนไซม์ 3.0 | 80 ไมโครลิตร | 240 ไมโครลิตร | 960 ไมโครลิตร |
| 12194-ค | ลิเกชั่นพร้อมผสม | 200 ไมโครลิตร | 600 ไมโครลิตร | 3800 ไมโครลิตร |
| 12194-ง | มิกซ์ขยายเสียง Ultima HF 2× | 200 ไมโครลิตร | 600 ไมโครลิตร | 3800 ไมโครลิตร |
-บันทึก- ส่วนประกอบของชุดเข้ากันได้กับทั้งสอง อิลลูมิน่า &เอ็มจีไอ แพลตฟอร์มการจัดลำดับ หากอะแดปเตอร์ครบชุด ถูกใช้ไปแล้ว ไฮฟ์ เอ็นจีเอสทีเอ็ม ไพรเมอร์มิกซ์ (
พื้นที่จัดเก็บ
ควรเก็บผลิตภัณฑ์นี้ไว้ที่ -25~-15℃ เป็นเวลา 1 ปี.
หมายเหตุ
1. เกี่ยวกับการดำเนินการ
1. โปรดปฏิบัติงานโดยสวมเสื้อคลุมแล็บและถุงมือแบบใช้แล้วทิ้ง-เพื่อความปลอดภัยของคุณ
2. ละลายส่วนประกอบที่อุณหภูมิห้อง หลังจากละลายแล้ว ให้ผสมให้เข้ากันโดยใช้เครื่องวอร์เท็กซ์ หมุนหลอดสั้นๆ แล้ววางลงบนน้ำแข็งเพื่อใช้ในภายหลัง
3. เมื่อเตรียมสารละลายปฏิกิริยาในแต่ละขั้นตอน แนะนำให้ใช้ปิเปตเพื่อผสมให้เข้ากันหรือเขย่าเบาๆ การเขย่าแรงๆ อาจทำให้ปริมาณสารในห้องสมุดลดลง
4. ขอแนะนำให้ใช้ปลายปิเปตแบบกรองเพื่อหลีกเลี่ยงการปนเปื้อนข้าม ควรเปลี่ยนปลายปิเปตเมื่อประมวลผลตัวอย่างที่แตกต่างกัน
5. การดำเนินการที่ไม่เหมาะสมอาจทำให้เกิดการปนเปื้อนของละอองลอย ซึ่งส่งผลต่อความแม่นยำของผลลัพธ์ แนะนำให้แยกบริเวณการผสมปฏิกิริยา PCR และบริเวณการทดสอบการทำให้บริสุทธิ์ผลิตภัณฑ์ PCR ออกจากกันทางกายภาพโดยบังคับ ติดตั้งอุปกรณ์ เช่น ปิเปตเฉพาะทางสำหรับการสร้างห้องสมุด ทำความสะอาดตามปกติสำหรับแต่ละพื้นที่โดยเช็ดพื้นผิวด้วยโซเดียมไฮโปคลอไรต์ 0.5% หรือสารฟอกขาว 10%
6. ผลิตภัณฑ์นี้ใช้เพื่อการวิจัยเท่านั้น
2. การแตกตัวของดีเอ็นเอ
1. ชุดนี้ใช้ได้กับ 100 หน้า - DNA อินพุต 1,000 นาโนกรัม ขอแนะนำให้ใช้ DNA อินพุตคุณภาพสูงที่มี A260/A280 = 1.8-2.0
2. การทดลองต่อไปนี้อาจได้รับผลกระทบหากนำเกลือที่มีความเข้มข้นสูง เช่น สารคีเลตโลหะ เข้ามาผสมกับดีเอ็นเอที่ป้อนเข้า เราขอแนะนำให้นำตัวอย่างดีเอ็นเอออกมา ดีดีเอช2โอ้ เพื่อการแตกกระจาย
3. กรุณาดูตาราง 6 สำหรับเวลาการแตกตัวของตัวอย่าง DNA มาตรฐาน ชุดทดสอบนี้มีค่าอคติการแตกตัวต่ำและครอบคลุม GC อย่างสม่ำเสมอสำหรับตัวอย่าง DNA ที่มีองค์ประกอบ GC หลากหลาย กรุณาปรับเวลาการแยกส่วนให้เหมาะสมกับความต้องการในการทดลองของคุณ
4. เพื่อให้การแตกตัวแม่นยำ โปรดเตรียมปฏิกิริยาบนน้ำแข็ง
3. อะแดปเตอร์ผูก
1. ชุด Illumina หรือ MGI Long Adapter (Barcoded Adapter) และชุด Short Adapter มีให้เลือกใช้ตามความต้องการในการทดลองของพวกเขา
2. ขอแนะนำให้เลือกใช้อะแดปเตอร์เชิงพาณิชย์ที่มีคุณภาพสูง หากเลือกอะแดปเตอร์ที่ผลิตเอง โปรดฝากบริษัทที่มีประสบการณ์ในการสังเคราะห์ไพรเมอร์ NGS และระบุถึงความจำเป็นในการควบคุมการปนเปื้อนอย่างเข้มงวด นอกจากนี้ ขอแนะนำให้เตรียมสารละลายแอนนีลลิ่ง DNA ในม้านั่งที่สะอาด และใช้อะแดปเตอร์เพียงชนิดเดียวในแต่ละครั้งเพื่อป้องกันการปนเปื้อนข้าม
3. โปรดละลายอะแดปเตอร์บนน้ำแข็งหรือที่อุณหภูมิ 4°C เมื่อใช้งานที่อุณหภูมิห้อง อุณหภูมิในห้องปฏิบัติการไม่ควรเกิน 25°C เพื่อป้องกันไม่ให้อะแดปเตอร์เสียสภาพ
4. คุณภาพและความเข้มข้นของอะแดปเตอร์จะส่งผลโดยตรงต่อประสิทธิภาพการเชื่อมต่อและผลผลิตของไลบรารี ความเข้มข้นของอะแดปเตอร์ที่สูงเกินไปจะเอื้อต่อการก่อตัวของไดเมอร์ของอะแดปเตอร์ ในขณะที่อะแดปเตอร์ที่น้อยเกินไปจะลดอัตราการเชื่อมต่อและผลผลิตของไลบรารี การเจือจางที่สอดคล้องกันกับบัฟเฟอร์ TE ตามปริมาณ DNA อินพุตเมื่อใช้อะแดปเตอร์ ตาราง 1-2 แสดงรายการวิธีการเจือจางที่แนะนำสำหรับอะแดปเตอร์ทั่วไปและ UMI สำหรับปริมาณ DNA อินพุตที่แตกต่างกันโดยใช้ชุดนี้สำหรับแพลตฟอร์มการจัดลำดับ Illumina หรือ MGI
โต๊ะ 1 อิลลูมิน่าที่แนะนำ จำนวนอะแดปเตอร์สำหรับอินพุตที่แตกต่างกัน ดีเอ็นเอ
| ป้อนข้อมูล ดีเอ็นเอ | ซีอัตราส่วนการเจือจางอะแดปเตอร์ทั่วไป | ความเข้มข้น | อัตราส่วนการเจือจางอะแดปเตอร์ UMI | ความเข้มข้น |
| 1 นาโนกรัม | 7.5 พับ | 2 ไมโครโมลาร์ | 15 เท่า | 1 ไมโครโมลาร์ |
| 1 ง ~ 10 นาโนกรัม | 3 พับ | 5 ไมโครโมลาร์ | 3 พับ | 5 ไมโครโมลาร์ |
| 10 ง - 200 ง | 1.5 พับ | 10 ไมโครโมลาร์ | 2 พับ | 7.5 ไมโครโมลาร์ |
| 200 นาโนกรัม | 0-พับ | 15 ไมโครโมลาร์ | 0-พับ | 15 ไมโครโมลาร์ |
โต๊ะ 2 คำแนะนำ เอ็มจีไอ จำนวนอะแดปเตอร์สำหรับอินพุตที่แตกต่างกัน ดีเอ็นเอ
| ป้อนข้อมูล ดีเอ็นเอ | ซีอัตราส่วนการเจือจางอะแดปเตอร์ทั่วไป | ความเข้มข้น | อัตราส่วนการเจือจางอะแดปเตอร์ UMI | ความเข้มข้น |
| 1 นาโนกรัม | 5 พับ | 2 ไมโครโมลาร์ | 10 เท่า | 1 ไมโครโมลาร์ |
| 1 ง ~ 10 นาโนกรัม | 2 พับ | 5 ไมโครโมลาร์ | 2 พับ | 5 ไมโครโมลาร์ |
| 10 ง - 200 ง | 0-พับ | 10 ไมโครโมลาร์ | 1.25 เท่า | 8 ไมโครโมลาร์ |
| 200 นาโนกรัม | 0-พับ | 10 ไมโครโมลาร์ | 0-พับ | 10 ไมโครโมลาร์ |
4. การทำความสะอาด DNA และการเลือกขนาดตามลูกปัด
1. การเลือกขนาด DNA สามารถทำได้ก่อนการซ่อมแซมปลาย/การหาง dA หลังการผูกอะแดปเตอร์ หรือหลังการขยาย
2. ขอแนะนำให้ดำเนินการเลือกขนาดทันทีหลังจากการผูกอะแดปเตอร์หากปริมาณ DNA อินพุตมากกว่า 50 นาโนกรัม มิฉะนั้นกรุณาเลือกขนาดหลังจากขยาย
3. สารเพิ่มประสิทธิภาพการรัดท่อประกอบด้วย PEG ที่มีความเข้มข้นสูง ซึ่งอาจส่งผลกระทบอย่างมีนัยสำคัญต่อการเลือกขนาดที่แม่นยำ ดังนั้น หากต้องเลือกขนาดทันทีหลังการรัดท่อด้วยอะแดปเตอร์ ขอแนะนำอย่างยิ่งให้เพิ่มขั้นตอนการทำความสะอาดเม็ดบีดก่อนการเลือกขนาด ขั้นตอนการเลือกขนาดสามารถดำเนินการได้โดยตรงหากดำเนินการก่อนการซ่อมแซมปลายท่อ/การต่อ dA หรือหลังจาก การขยายห้องสมุด
4. ควรปรับสมดุลลูกปัดแม่เหล็กที่อุณหภูมิห้องก่อนใช้งาน มิฉะนั้น ผลผลิตจะลดลง และผลการเลือกขนาดจะได้รับผลกระทบ
5. ควรผสมลูกปัดแม่เหล็กให้เข้ากันโดยใช้วิธีวอร์เท็กซ์หรือปิเปตก่อนใช้งาน
6. ห้ามดูดลูกปัดออกเมื่อถ่ายโอนของเหลวส่วนบน แม้ว่าจะมีลูกปัดเพียงเล็กน้อยก็อาจส่งผลต่อปฏิกิริยาต่อไปนี้ได้
7. ควรเตรียมเอธานอล 80% ใหม่ๆ มิฉะนั้น จะส่งผลต่อประสิทธิภาพการกู้คืน
8. เพื่อให้เลือกขนาดได้แม่นยำ ขอแนะนำให้เริ่มด้วยปริมาตรมากกว่า 100 μL หากน้อยกว่านี้ ขอแนะนำให้เพิ่มปริมาตรเป็น 100 μL ด้วยน้ำบริสุทธิ์พิเศษ
9. ควรทำให้ลูกปัดแม่เหล็กแห้งที่อุณหภูมิห้องก่อนทำการชะผลิตภัณฑ์ออก หากผลิตภัณฑ์แห้งไม่เพียงพอ อาจทำให้เอธานอลที่เหลือส่งผลต่อปฏิกิริยาที่เกิดขึ้นในภายหลังได้ง่าย หากแห้งมากเกินไป ลูกปัดแม่เหล็กจะแตกร้าวและลดปริมาณการฟอกให้บริสุทธิ์ โดยปกติแล้ว ควรทำให้ลูกปัดแห้งที่อุณหภูมิห้องเป็นเวลา 3-5 นาทีก็เพียงพอที่จะทำให้ลูกปัดแห้งสนิท
10. หากจำเป็น ตัวอย่าง DNA ที่ผ่านการทำให้บริสุทธิ์หรือเลือกขนาดจะถูกชะออกมา 0.1× สามารถเก็บบัฟเฟอร์ TE ที่อุณหภูมิ 4°C ได้นาน 1-2 สัปดาห์ หรือที่อุณหภูมิ -20°C ได้นาน 1 เดือน
5. การขยายเสียงห้องสมุด
1. การขยายไลบรารีหรือไม่นั้นขึ้นอยู่กับปริมาณอินพุตของ DNA ประเภทของอะแดปเตอร์ แอปพลิเคชันข้อมูลการจัดลำดับ ฯลฯ จำเป็นต้องทำขั้นตอนการขยายหากใช้อะแดปเตอร์บางส่วน เมื่อใช้อะแดปเตอร์แบบเต็มความยาว หากอินพุต DNA < 200 นาโนกรัม ขอแนะนำให้ทำการขยาย มิฉะนั้น ไม่จำเป็นต้องทำการขยาย
2. จำนวนรอบการขยายสัญญาณควรได้รับการควบคุมอย่างเคร่งครัด การขยายสัญญาณที่ไม่เพียงพออาจส่งผลให้ผลผลิตของไลบรารีต่ำ การขยายสัญญาณมากเกินไปอาจทำให้เกิดอคติ ข้อผิดพลาด การอ่านซ้ำ และผลิตภัณฑ์ไคเมอริกที่เพิ่มขึ้น ตาราง 3 แสดงรายการหมายเลขรอบที่แนะนำโดยตั้งเป้าผลผลิตของห้องสมุดที่ 1 μg
โต๊ะ 3 จำนวนรอบที่แนะนำในการสร้าง ผลผลิตห้องสมุด 1,000 นาโนกรัม
| อินพุตดีเอ็นเอ | จำนวนรอบที่จำเป็นในการสร้างผลผลิตห้องสมุด 1 μg |
| 1000-2000 ง | 2 - 4 |
| 500 นาโนกรัม | 2 - 4 |
| 250 นาโนกรัม | 4 - 6 |
| 100 นาโนกรัม | 5 - 7 |
| 50 นาโนกรัม | 7 - 9 |
| 10 ง | 9 - 11 |
| 5 ง | 10 - 12 |
| 1 นาโนกรัม | 12 - 15 |
| 100 หน้า | 16 - 18 |
บันทึก
1.ตาราง 3 แสดงจำนวนพารามิเตอร์ลูปโดยใช้การทดสอบ DNA อินพุตคุณภาพสูงประมาณ 200 bp คุณภาพของ DNA FFPE แตกต่างกันอย่างมาก และเมื่อคุณภาพของ DNA ไม่ดีหรือความยาวของไลบรารียาว จำนวนรอบจะต้องเพิ่มขึ้นอย่างเหมาะสมเพื่อให้ได้ไลบรารีที่เพียงพอ
2. หากจำเป็นต้องเลือกขนาดในระหว่างกระบวนการสร้างห้องสมุด แนะนำให้ใช้หมายเลขรอบที่สูงกว่าสำหรับการขยายห้องสมุด ในกรณีอื่นๆ แนะนำให้ใช้หมายเลขรอบที่น้อยกว่า
3. หากใช้อะแดปเตอร์ที่ไม่สมบูรณ์ จะต้องขยายอย่างน้อย 2 วงจรเพื่อสร้างอะแดปเตอร์ที่สมบูรณ์
6. การวิเคราะห์คุณภาพห้องสมุด
1. คุณภาพของห้องสมุดที่สร้างขึ้นโดยทั่วไปจะได้รับการวิเคราะห์โดยการวัดความเข้มข้นและการกระจายขนาด
2. สามารถวัดความเข้มข้นของห้องสมุดได้ด้วยวิธีที่ใช้สารเรืองแสง เช่น Qubit และ PicoGreen หรือ qPCR
3. ไม่แนะนำให้ใช้การวัดปริมาณตามการดูดกลืนแสง เช่น NanoDrop
4. แนะนำให้ใช้วิธี qPCR สำหรับการวัดปริมาณไลบรารี: วิธีที่ใช้ฟลูออเรสเซนต์ เช่น Qubit และ PicoGreen ไม่สามารถแยกความแตกต่างระหว่างโครงสร้าง dsDNA ที่ไม่สมบูรณ์ (ส่วนที่แทรกโดยไม่มีอะแดปเตอร์หรือส่วนที่ปลายด้านใดด้านหนึ่งถูกผูกด้วยอะแดปเตอร์) จากไลบรารีที่สมบูรณ์ได้ วิธี qPCR จะขยายและวัดไลบรารีที่สมบูรณ์โดยที่ปลายทั้งสองข้างถูกผูกด้วยอะแดปเตอร์เท่านั้น (ไลบรารีที่เรียงลำดับได้) ซึ่งจะทำให้การวัดปริมาณโหลดมีความแม่นยำมากขึ้น
5. สามารถวิเคราะห์การกระจายขนาดของห้องสมุดได้โดยใช้ Agilent Bioanalyzer หรืออุปกรณ์อื่นๆ ที่ใช้หลักการของอิเล็กโทรโฟรีซิสแบบเส้นเลือดฝอยหรือไมโครฟลูอิดิกส์
7. วัสดุอื่นๆ
1. ลูกปัดแม่เหล็กทำความสะอาด DNA: Hieff NGSทีเอ็ม ลูกปัดคัดแยกดีเอ็นเอ (
2.อะแดปเตอร์: อะแดปเตอร์ครบชุดสำหรับ Illumina:
3. การวิเคราะห์คุณภาพห้องสมุด: Agilent 2100 Bioanalyzer DNA 1000 Chip/High Sensitivity Chip หรือผลิตภัณฑ์เทียบเท่าอื่น ๆ; สารเคมีเชิงปริมาณในห้องสมุด
4. วัสดุอื่นๆ: เอธานอลบริสุทธิ์ น้ำบริสุทธิ์ที่ผ่านการฆ่าเชื้อ ปลายปิเปตที่มีการกักเก็บต่ำ หลอด PCR ขาตั้งแม่เหล็ก เครื่องปั่นความร้อน ฯลฯ
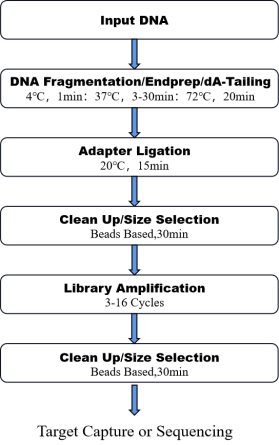
8. เวิร์กโฟลว์
รูปที่ 1. เวิร์กโฟลว์ของ วันพ็อต โปร ดีเอ็นเอ ชุดเตรียมเข้าห้องสมุด
ตัวเลข
ขนาดของชิ้นส่วนแทรกที่ได้รับภายใต้เงื่อนไขการแตกชิ้นส่วนที่แตกต่างกัน
โดยใช้ gDNA มาตรฐาน 500 นาโนกรัมเป็นแม่แบบ ห้องสมุดจึงถูกสร้างขึ้นโดยใช้ชุดนี้ เงื่อนไขการแตกตัวคือการย่อยด้วยเอนไซม์ที่อุณหภูมิ 32°C, 35°C และ 37°C เป็นเวลา 5, 10, 15, 20 และ 30 นาทีตามลำดับ ผลิตภัณฑ์ที่แตกตัวได้รับการทำให้บริสุทธิ์ด้วยลูกปัดแม่เหล็ก 1.2 เท่า และชะออกด้วย ddH 21 μL2O. ความเข้มข้นถูกวัดโดยใช้ Qubit และการกระจายตัวของชิ้นส่วนแทรกที่กู้คืนมาจะแสดงในรูปต่อไปนี้
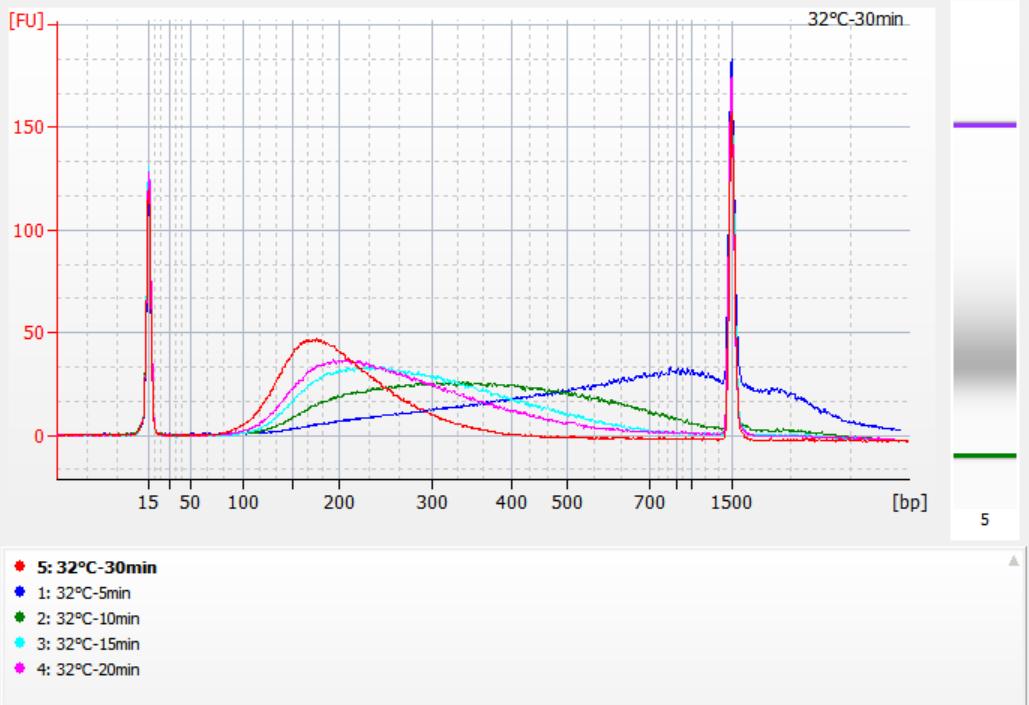 |
รูปที่ 2 โปรไฟล์ไลบรารีที่ 32°C สำหรับเวลาการย่อยเอนไซม์ที่แตกต่างกัน
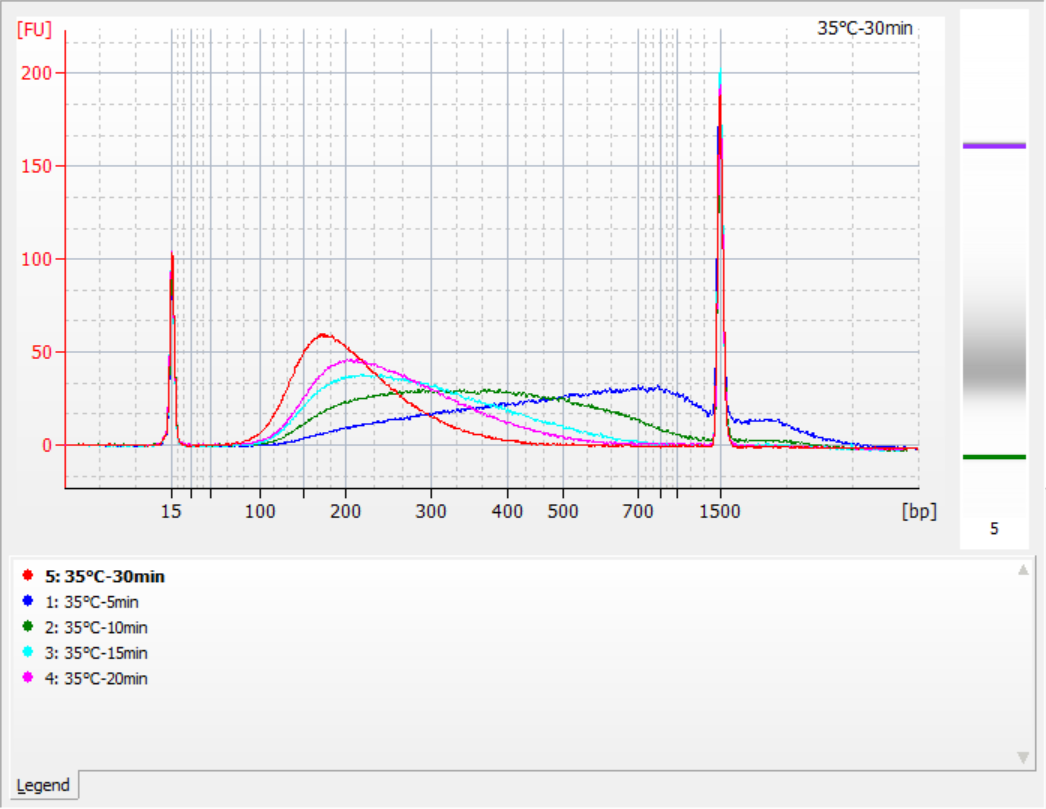 |
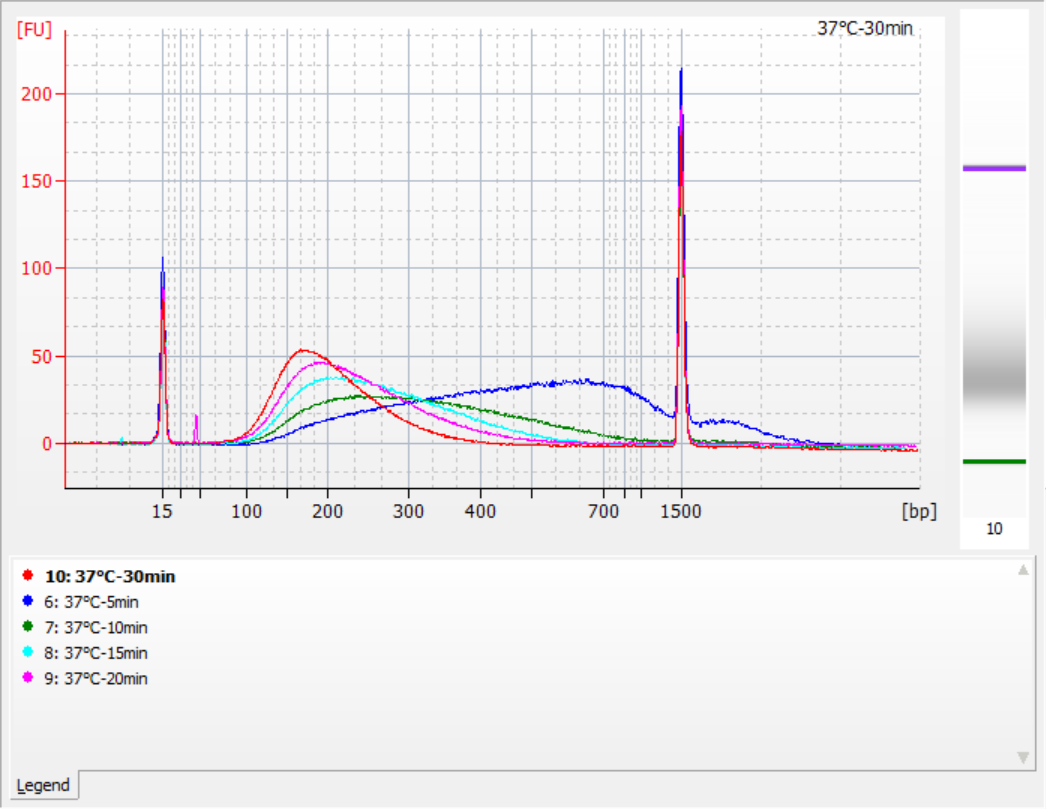 |
การชำระเงินและความปลอดภัย
ข้อมูลการชำระเงินของคุณได้รับการดำเนินการอย่างปลอดภัย เราไม่เก็บรายละเอียดบัตรเครดิตและไม่สามารถเข้าถึงข้อมูลบัตรเครดิตของคุณได้
การสอบถาม
คุณอาจชอบ
คำถามที่พบบ่อย
ผลิตภัณฑ์นี้มีวัตถุประสงค์เพื่อการวิจัยเท่านั้น และไม่ได้มีวัตถุประสงค์เพื่อใช้ในการรักษาหรือวินิจฉัยโรคในมนุษย์หรือสัตว์ ผลิตภัณฑ์และเนื้อหาได้รับการคุ้มครองโดยสิทธิบัตร เครื่องหมายการค้า และลิขสิทธิ์ที่เป็นของ
แอปพลิเคชั่นบางตัวอาจต้องใช้สิทธิ์ในทรัพย์สินทางปัญญาของบุคคลที่สามเพิ่มเติม