DNase I et leurs applications en biomédecine
La désoxyribonucléase I (DNase I) est une endonucléase dont l'application ne se limite pas à maintenir l'intégrité de l'ARN, mais également à analyser l'empreinte de l'ADN, à générer des bibliothèques d'ADN aléatoires, à réduire l'adhérence des lysats cellulaires ou des extraits de protéines, etc. En un mot, la DNase I peut être utilisée dans presque toutes les applications qui nécessitent des clivages enzymatiques de l'ADN. Voici une introduction détaillée à la DNase I et à son application spécifique.
1. Qu'est-ce que la DNase I ?
2. DNase I pour la préparation de l'extraction d'ARN sans ADN
3. DNase I pour la transcription in vitro afin d'éliminer l'ADN matrice
4. DNase I pour l'élimination de l'ARNr
5. DNase I pour le marquage de l'ADN
6. Autres applications
7. Guide de sélection des produits DNase I
1. Qu'est-ce que la DNase I ?
Désoxyribonucléase I (DNase I) est une endonucléase non spécifique qui peut digérer l'ADN simple ou double brin, présent dans différents tissus et fluides corporels. Elle peut hydrolyser les liaisons phosphodiester pour produire des mono- et oligodésoxynucléotides contenant un groupe 5'-phosphate et un groupe 3'-OH. La plage de pH de travail optimale de la DNase I est de 7-8, son activité dépend du Ca2+ et peut être activée par des ions métalliques divalents tels que Mn2+, Mg2+, Zn2+, etc. En présence de Mg2+, la DNase I cisaille de manière aléatoire n'importe quel site d'ADN double brin ; en présence de Mn2+, la DNase I peut cisailler l'ADN double brin au même site pour former une extrémité franche ou des extrémités collantes de 1 à 2 nucléotides.
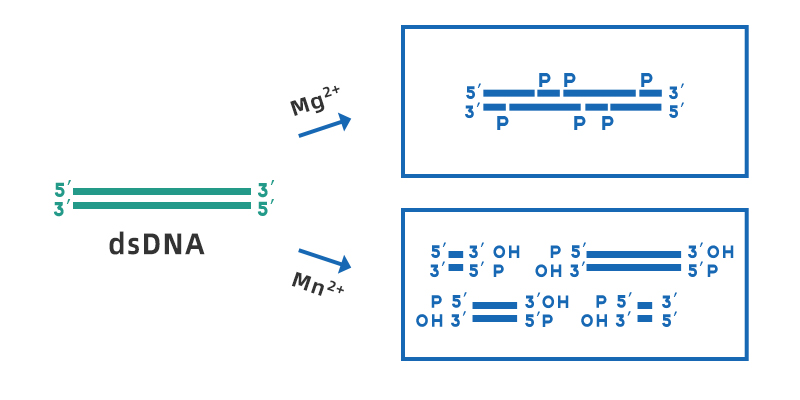
Figure 1. Schéma du clivage de l'ADNdb par la DNase I en présence de Mg2+ et Mn2+.
Bien que les clivages de la DNase I soient généralement considérés comme des clivages non spécifiques, la DNase I est plus susceptible d'agir sur certains fragments de séquence, tels que la région du petit sillon, et est plus susceptible de cliver les séquences purine-pyrimidine. Cependant, lorsque la DNase I agit sur un ADNds hétérogène, les quatre bases seront clivées et l'effet sur une base spécifique ne sera pas plus de 3 fois supérieur à celui des autres bases.
2. DNase I pour la préparation de l'extraction d'ARN sans ADN
Dans les expériences biologiques, la première étape consiste à préparer l'acide nucléique pour étudier les différentes fonctions de l'ARN. Cependant, comme l'ADN et l'ARN sont souvent libérés ensemble au cours du processus de lyse cellulaire, l'interférence entre les deux ne peut être évitée, quelle que soit la solution d'extraction utilisée. Il faut donc utiliser des enzymes spécifiques pour éliminer l'interférence. Pour une extraction d'ARN de haute qualité, la DNase I est utilisée pour éliminer l'ADN résiduel de l'échantillon.
La DNase I peut dégrader l'ADN double brin et simple brin en oligonucléotides et nucléotides simples, et l'ADN dans le produit de préparation d'ARN peut être efficacement dégradé. La DNase I est ensuite inactivée par chauffage avec un tampon d'arrêt. Pendant le processus de chauffage, la structure en épingle à cheveux de la molécule d'ARN peut être ouverte, ce qui facilite l'entrée directe de l'ARN dans le processus de transcription inverse.
La qualité de l'ARN aura une incidence directe sur les données expérimentales dans une large mesure. En général, les résidus d'ADNg ne peuvent pas être complètement évités lors de l'extraction de l'ARN. Par conséquent, il est généralement recommandé de traiter les échantillons d'ARN avec de la DNase I pour digérer l'ADNg résiduel avant de procéder à des applications en aval (par exemple, analyse de l'expression de l'ARNm, analyse du transcriptome, etc.). L'étape de digestion de l'ADNg peut être réalisée pendant l'extraction de l'ARN, après l'extraction de l'ARN ou avant la transcription inverse de l'ARN.Selon le positionnement du produit, les produits fournis par Yeasen sont les suivants :
Tableau 1 : Liste des produits liés à l'élimination de l'ADN, à l'extraction de l'ARN ou avant la transcription inverse
| Positionnement du produit | Nom du produit | Chat # |
| Extraction d'ARN | Réactif d'extraction d'ARN total TRIeasy™ [renseigner] | 10606ES |
| 19221ES | ||
| Kit ARN MolPure™ Plant Plus [renseigner] | 19292ES | |
| Kit d'ADN/ARN viral MolPure™ [renseigner] | 19321ES | |
| Suppression de l'ADN génomique | 10325ES | |
| Transcription inverse | Hifair™Ⅲ SuperMix de synthèse d'ADNc 1er brin pour qPCR (digesteur d'ADNg plus) | 11141ES |
| PCR quantitative | 11184ES |
3. DNase I pour la transcription in vitro afin d'éliminer l'ADN matrice
La transcription in vitro (IVT) utilise principalement l'ADN comme modèle, ainsi que les substrats et tampons correspondants pour obtenir l'ARN par transcription in vitro. Dans les expériences de transcription in vitro, les ARN polymérases telles que T7, T3 et SP6 sont couramment utilisées pour la synthèse de l'ARN. L'ARN synthétisé peut contenir des résidus d'ADN. L'élimination des résidus d'ADN est bénéfique pour le développement des expériences en aval. Par exemple, au stade du développement du vaccin à ARNm, l'élimination des résidus est une étape critique, qui peut réduire la difficulté de la purification en aval et augmenter la pureté du produit. Le modèle d'ADN est généralement éliminé à l'aide de la DNase I recombinante (sans RNase).Selon le processus de synthèse de l'ARNm, les produits fournis par Yeasen sont les suivants :
| Processus de synthèse de l'ARNm | Nom du produit | Chat# |
| Préparation du modèle | ADN polymérase haute fidélité Hieff Canace™ Plus [renseigner] | 10148ES |
| 10922ES | ||
| 10125ES | ||
| FuniCut™BsaI [renseigner] | 15005ES | |
| FuniCut™ XbaI [renseigner] | 15033ES | |
| BspQI[demande] [renseigner] | 16215ES | |
| Transcription in vitro | 10623ES | |
| 10624ES | ||
| ARN polymérase T7 (50 U/μL)[renseigner] | 10618ES | |
| 10133ES | ||
| 10620ES | ||
| 10621ES | ||
| Supprimer l'ADN modèle | 10611ES | |
| Modification de l'ARNm | Enzyme de coiffage de l'ARNm de la vaccine UCF.ME™ de qualité GMP | 10614ES |
| Capuchon d'ARNm UCF.ME™ 2'-O-méthyltransférase de qualité GMP | 10612ES | |
| 10132ES | ||
| 10619ES | ||
| Purification de l'ARNm | 12602ES |
4. DNase I pour l'élimination de l'ARNr
In vivo, l'ARNr est très abondant et très conservateur, ce qui n'a que peu d'importance pour obtenir des informations biologiques. C'est pourquoi l'ARNr est souvent éliminé en premier lors de la construction et du séquençage de la bibliothèque d'ARN.Actuellement, la méthode d'élimination de l'ARNr est principalement la digestion par la RNase H. Les principales étapes de l'épuisement enzymatique de l'ARNr sont présentées dans la figure 2 :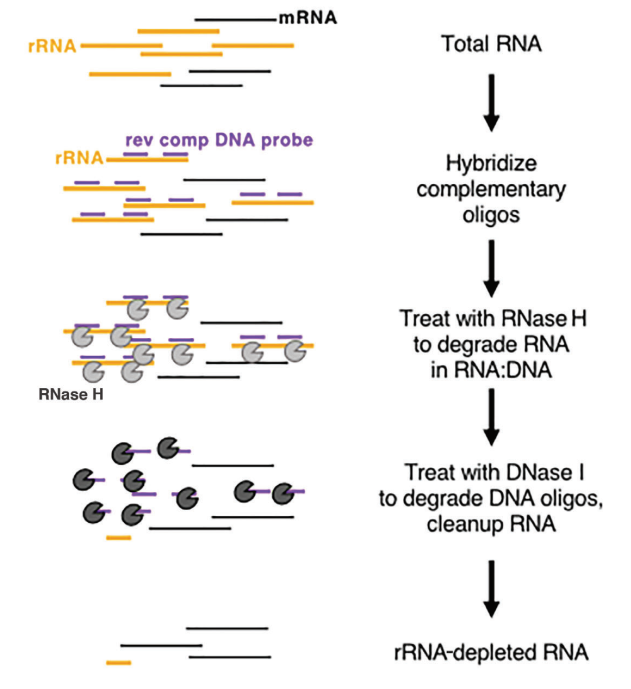
Figure 2 : Schéma du principe de l'épuisement enzymatique de l'ARNr (Baldwin, A. et al. 2021, Current Protocols)
Tout d'abord, extraire l'ARN total, puis hybrider la sonde d'ADN monocaténaire avec l'ARNr, concevoir et synthétiser la sonde d'ADN monocaténaire spécifique à l'ARNr, puis utiliser la RNase H pour dégrader l'ARNr hybridé et utiliser la DNase I pour dégrader la sonde d'ADN. Enfin, laisser le modèle d'ARN non-ARNr. Les produits liés à l'élimination de l'ARNr fournis par Yeasen sont les suivants :
| Processus de synthèse de l'ARNm | Nom du produit | Chat# |
| Humain/Souris/Rat Épuisement de l'ARNr | Système de surveillance de la glycémie haute performance (NGS) de Hieff Kit de déplétion d'ARNr MaxUp (humain/souris/rat) MaxUp [renseigner] | 12253ES |
| Épuisement de l'ARNr des plantes | 12254ES | |
| Élimination de l'ARN ribosomique et des régions 45S ITS/ETS de l'ARN total humain | 12257ES | |
| Dégradation de l'ARNr | 12906ES | |
| Dégradation de la sonde ADN | 10325ES |
5.DNase I pour le marquage de l'ADN
La translation de nick est l'une des méthodes de marquage de sondes d'acide désoxyribonucléique les plus couramment utilisées en laboratoire. Cette méthode utilise diverses activités enzymatiques de l'ADN polymérase I pour incorporer des désoxyribonucléosides triphosphates marqués dans des chaînes d'ADN nouvellement synthétisées. Ainsi, des sondes d'ADN uniformément marquées pour une activité spécifique élevée sont synthétisées. Les caractéristiques de la translation de nick sont rapides, simples, délibérées, hautement spécifiques et des sondes uniformément marquées, qui conviennent à l'ADN double brin plus long.La méthode est réalisée par l'action combinée de la DNase I et de l'ADN polymérase I d'E. coli. Les principales étapes du marquage de l'ADN par translation de coupure sont présentées dans la figure 3 :
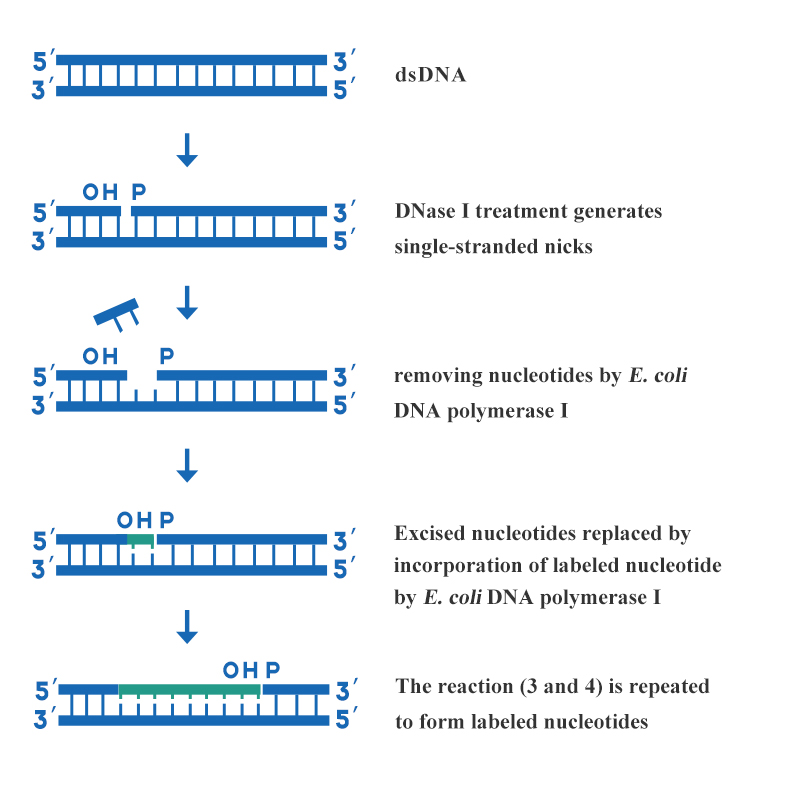
Figure 3 : Schéma de l'étiquetage de l'ADN par translation de coupure
Une concentration appropriée de DNase I est utilisée pour créer plusieurs espaces monocaténaires sur chaque brin de l'ADN double brin à marquer, et l'extrémité hydroxyle 3' est formée au niveau de l'espace. Utilisez l'activité exonucléase 5'→3' de l'ADN polymérase I d'E. coli pour couper un nucléotide de l'extrémité 5' de l'entaille, et en même temps l'activité polymérase 5'→3' de l'ADN polymérase I d'E. coli introduit un nucléotide marqué avec l'extrémité 3' de l'espace pour réparer l'espace. Au fur et à mesure que l'espace se déplace le long du brin d'ADN, les nucléotides marqués sont incorporés dans le brin nouvellement synthétisé.Les produits liés à l'étiquetage ADN fournis par Yeasen sont les suivants :
| Positionnement du produit | Nom du produit | Chat# |
| Ordinaire | Désoxyribonucléase I (DNase I) du pancréas bovin [renseigner] | 10607ES/10608ES |
| Sans RNase | 10325ES | |
| E.coli source | 12903ES |
6. Autres applications
Les applications ci-dessus sont couramment utilisées. D'autres applications de la DNase I incluent les suivantes, telles que le test d'empreinte de la DNase I et les sites hypersensibles à la DNase I. Le test d'empreinte de la DNase I est une méthode de détection qui peut identifier avec précision les sites de liaison des protéines de liaison à l'ADN sur l'ADN. Lorsqu'une protéine se lie à un fragment d'ADN, elle peut protéger le site de liaison contre les dommages causés par la DNase I et les fragments d'ADN seront laissés derrière après la digestion enzymatique (« empreinte »), et sa séquence peut être déterminée. Dans l'image du gel, il n'y a pas de bandes où l'ADN se lie à la protéine. Pour en savoir plus, cliquez sur le lien.Les sites hypersensibles à la DNase I se réfèrent aux clivages sur un petit nombre de sites spécifiques lorsque la chromatine est traitée avec une faible concentration de DNase I et ces sites spécifiques sont appelés sites hypersensibles à la DNase I. Le principe est que lorsqu'un gène est dans un état transcriptionnellement actif, la chromatine contenant le gène est significativement plus sensible à la dégradation par la DNase que la région inactive. Pour en savoir plus, cliquez sur le lien.
7. Guide de sélection des produits DNase I
Fondée en 2014, Yeasen Biotechnology (Shanghai) Co., Ltd. est une entreprise de haute technologie spécialisée dans la recherche et le développement et la production de matières premières enzymatiques et d'anticorps antigéniques. Ses produits comprennent des enzymes de diagnostic moléculaire, des protéines et des anticorps utilisés dans les produits pharmaceutiques, les tests de sécurité alimentaire, l'élevage, la justice et d'autres industries. Nous nous engageons à fournir aux clients du domaine des sciences de la vie des produits et services de haute qualité. Les directives d'achat de produits pour DNase I sont les suivantes :| Nom du produit (Cat#) | Positionnement du produit | Applications recommandées |
| DNase I du pancréas bovin (CAT#10607,10608)[renseigner] | RNase supprimée, non détectée | Principalement utilisé dans la recherche sur les protéines : élimination de l'ADN des préparations protéiques. |
| DNase I recombinante (sans RNase)(CAT#10325) | Sans RNase, pour la recherche | Idéal pour une variété d'applications : élimination d'ADN à partir de préparations d'ARN et de protéines telles que les bibliothèques d'ADNc sensibles à la RNase ou préparation d'échantillons pour des expériences de RT-PCR. |
| UCF.ME™Désoxyribonucléase I (DNase I) de qualité GMP(CAT#10611) | Sans RNase, qualité pharmaceutique GMP. | Idéal pour une variété d'applications : élimination d'ADN à partir de préparations d'ARN et de protéines telles que les bibliothèques d'ADNc sensibles à la RNase ou préparation d'échantillons pour des expériences de RT-PCR. |
Concernant la lecture :
Réactifs de qualité GMP pour la synthèse in vitro d'ARNm
Les principes de l'empreinte DNase I et ses applications biomédicales
Références
1. Baldwin A, Morris AR, Mukherjee N. Une méthode simple, économique et évolutive pour épuiser l'ARN ribosomique humain pour l'ARN-seq[J]. Protocoles actuels, 2021.
2. Song C, Zhang S, Huang H. Choisir une méthode appropriée pour l'identification des origines de réplication dans les génomes microbiens[J]. Frontiers in Microbiology, 2015, 6:1049.
